- [SHARE]
- ツイート


最終回 効率のよい転写反応:マグネシウムイオンと基質の量
RNA干渉やアプタマー,そしてRNA新大陸など,RNAの幅広い研究が盛んになり,その調製法の1つである転写反応はRNA研究者にとってルーティンワークになっている.各社から転写キットも販売され,プロトコールもキットごとにほぼ確立しているといってよいだろう.しかし効率のよい転写を行うには,いくつかの注意点がある.今回は,転写におけるマグネシウムイオンと基質の量について調べてみた.
T7 RNAポリメラーゼによる転写
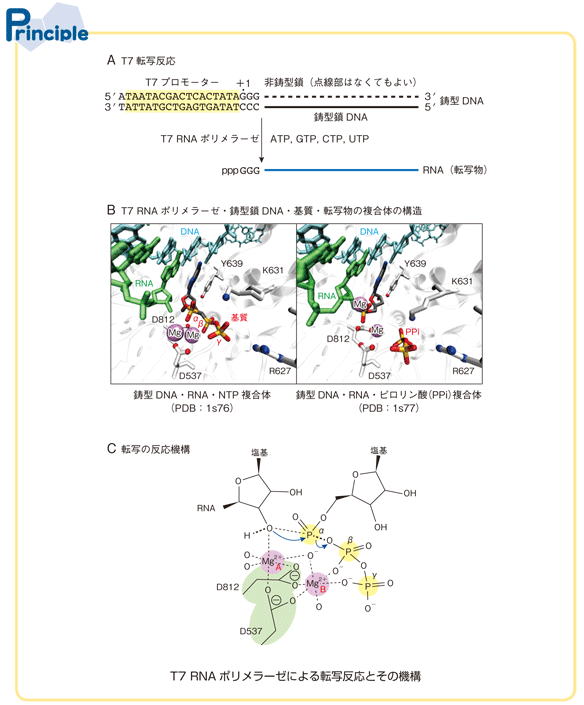
試験管内の転写反応で最も一般的なのがT7 RNAポリメラーゼを用いる方法だろう.大腸菌のバクテリオファージT7 にコードされたDNA依存RNAポリメラーゼ(T7 RNAポリメラーゼ)は,T7 プロモーター配列を含む二本鎖DNAを鋳型とし,ヌクレオシド三リン酸(NTP)を基質にしてプロモーターの下流の鋳型鎖DNAに相補的な一本鎖RNAを合成する(Principle A).反応には鋳型DNA,基質NTP,補因子として二価のマグネシウムイオン,そしてDTTなどの還元剤が必須である.その他,ポリメラーゼの安定化や活性化を助ける試薬として,スペルミジンなどのポリアミン(終濃度1~2 mM)や非イオン性界面活性剤であるTriton X-100(終濃度0.001 %~0.01 %)などを添加する場合もある.鋳型DNAには,完全長の二本鎖DNAを用いる場合とプロモーター領域のみ二本鎖化したものを用いる場合がある(Milligan, J. F. & Uhlenbeck,O. C.:Methods Enzymol., 180:51, 1989).
伸長するRNA鎖にヌクレオチドが付加するヌクレオチド転移反応では,ポリメラーゼの活性部位において,2つのマグネシウムイオン(A とB)が関与する機構が提唱されている(Castro, C. et al.:Proc. Natl.Acad. Sci. USA, 104:4267, 2007)(Principle B,C).マグネシウムイオンA はRNA鎖の3′末端付近に位置し,末端ヌクレオシドの3′位水酸基のpKa を下げることにより,基質のα位のリン酸に対する3′位水酸基の求核性を高めている. さらに,このマグネシウムイオンA は,ヌクレオチド転移反応で形成される5価のリン中間体(オキシアニオン)を安定化する役割も果たしている. マグネシウムイオンB は,オキシアニオンの安定化に加え,反応副産物(脱離基)として生じるピロリン酸(PPi)の解離を助ける.Principle B(左図)に,基質アナログ(ここでは非水解性のα,β - methylene ATP を用いている)・RNA鎖・鋳型鎖DNAを含むT7 RNAポリメラーゼの複合体の立体構造を示した.ここでは,活性部位に取り込まれた基質がヌクレオチド転移する直前の様子が示されている.Principle B(右図)は,基質のヌクレオチドとRNA鎖の3′末端水酸基の間でヌクレオチド転移反応が終了した状態を示している(Yin, Y. W. & Steitz, T. A.:Cell, 116:393, 2004).この2つのマグネシウムイオンの関与は,転写のみならず複製においても共通する重要な機構である.したがって,核酸合成酵素による反応では,マグネシウムイオンの添加が必須である.
転写におけるマグネシウムイオンと基質の量
マグネシウムイオンと基質の量は,各転写キットによって異なり,高効率の転写キットでは基質濃度を高くしている場合が多い.その際に基質の三リン酸部分にマグネシウムイオンが補足されるので,基質濃度が高くなるとマグネシウムイオンを増やす必要がある.また生成したRNA転写物のリン酸部位や生じたピロリン酸にもマグネシウムイオンが対イオンとして補足されるので,長鎖のRNAを大量に調製する際もマグネシウムイオンの濃度を高くする必要がある.一般的に鋳型DNAから200 倍量以上のRNAが得られる.Protocolには,われわれの研究室で行っている転写の手法(0.1 mL スケールの場合)を示した.17塩基の短いRNA断片と152塩基の比較的長いRNA断片の転写では,それぞれの基質の濃度が異なっている(また鋳型DNAの量も異なっている).基質の濃度に関しては,後述する実験例を参照していただきたい.
はじめに鋳型DNA溶液を準備するために,鋳型鎖のDNA断片と非鋳型鎖(コード鎖)のDNA断片のアニーリングを行う.100塩基以上のRNAの転写では,プラスミドを切断したDNAやPCR で増幅したDNAを鋳型に用いることが多い.短鎖のRNAの転写では,DNA合成機を用いて鋳型DNAを調製することが多いので非鋳型鎖はプロモーター部分のみの配列を用いる(われわれのグループでは,プロモーターの両側の配列を含む21塩基の非鋳型鎖DNAを用いている).転写開始の+1の部位はGにしないと転写量が激減する.したがってGTPスタートで転写がはじまるので,転写物の5′末端はグアノシン5′- 三リン酸になる.転写開始点からの3塩基はGGG にする場合が多く,ここにAやT を入れると転写量が減ってしまう(Principle A).また,T7 φ 2.5 プロモーターを用いることによりATPスタートにすることも可能である(Huang, F. et al.:Biochemistry, 39:15548, 2000).
鋳型DNA溶液に,基質溶液,緩衝液,Triton 系界面活性剤,塩化マグネシウム溶液をそれぞれ加え,最後にT7 RNAポリメラーゼを加えて転写反応を開始する.反応時間は短鎖のRNAの場合には2時間程度でもよいが,100塩基を超える長いRNA断片の場合には長時間(4~20時間)の方がよい(以下の実験例参照).反応液に尿素溶液を加えて転写を停止させ,この溶液がそのままゲル電気泳動用のローディング溶液になる.転写物をゲル電気泳動で精製するが,一般的に10塩基よりも短いRNA断片がかなり生じる.これは転写の前半でポリメラーゼが脱離しやすいためである(アボーティングという).また目的物よりも1~2塩基長い断片も得られることが多い.さらに鋳型DNAの配列のデザインが悪いと長鎖長の転写物が生成する場合もある(Cazenave, C. & Uhlenbeck, O. C.:Proc. Natl. Acad. Sci. USA, 91:6972, 1994).
実験例
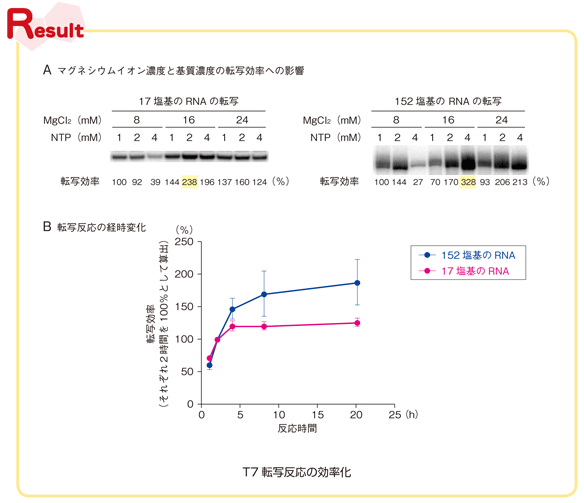
最初に17塩基と152塩基のRNAの転写について,基質濃度(1~4 mM)とマグネシウムイオン濃度(8~24 mM)が転写効率に及ぼす影響を調べた.転写は20 μ L のスケールで[ α -32P]UTP を加えて行い,転写物を内部標識することによりゲル電気泳動でRNAの生成量を調べた.本実験ではタカラバイオ社のT7 RNAポリメラーゼを用いた.タカラバイオ社のプロトコールではTriton 系の界面活性剤を加えていないが,実験の再現性を調べたところTriton X-100 を加えた方が安定した結果が得られた.すべての転写は37 ℃で2時間行い,3回の実験の平均値をResult A に示した.それぞれの転写反応で1 mM NTPと8 mM 塩化マグネシウムを用いた場合を基準にして,全長のRNA転写物の相対量を求めた.
17塩基のRNAでは2 mM NTPと16 mM 塩化マグネシウム,一方,152塩基のRNAでは4 mM NTPと16 mM 塩化マグネシウムを用いた場合が,本実験の範囲では転写量が最も多かった.どちらも8 mM 塩化マグネシウムの存在下では,NTPの濃度を4 mM まで上げてしまうと転写量が極端に減少する.これはNTPにマグネシウムイオンが補足されてしまい,反応に必要なマグネシウムイオンが不足するためだろう.またNTPの濃度は152塩基のRNAの方が高くなっているが,一般的に長鎖のRNAの方がNTP濃度に依存して転写効率が高まる傾向にある.市販のキットでは7.5mM のNTPを加えているものもある.高濃度のNTPを加える場合はマグネシウムイオン濃度も高くする必要があるが,転写後に生じたピロリン酸とマグネシウムイオンによる沈殿が反応系内に析出しやすくなる.われわれの実験でも152塩基の転写では,16 mM 以上のマグネシウムイオン存在下で転写後の溶液に沈殿が生じている.副産物のピロリン酸をピロホスファターゼで分解する方法もあるが,ゲル電気泳動のウェルに沈殿を入れてしまわない限り,転写反応中のリン酸マグネシウムの多少の析出は問題ない.
次に17塩基のRNAと152塩基のRNAの転写について,上記のそれぞれの最適条件を用いて転写効率の経時変化を調べた.Result B はそれぞれのRNAの転写反応が2時間の場合を100 %にして各反応時間における相対量をグラフにしている.したがってこのグラフから17塩基と152塩基のそれぞれのRNA間で転写効率を比較することはできないので注意されたい.短鎖の17塩基の転写では2時間の転写でも20時間の場合の8割ぐらいのRNAが得られ,4時間程で転写量がほぼ横ばいになることがわかった. 152塩基の転写では2時間と比較して20時間後に転写量が2倍近くまで増えている.しかし4時間で20時間の8割,8時間で9割の転写産物が得られる.これらの結果から,長鎖のRNAの転写では,基質量とともに反応時間も長め(4~20時間)にした方がよさそうである.
まとめ
すでに各社から転写キットが販売されているので,そのプロトコールにしたがってRNAを調製されている方も多いだろう.しかし,今回の結果からもわかるように,最適な転写条件は,作製するRNAの長さやスケールに応じて,基質量,マグネシウムイオン濃度,転写時間が異なる.最近は高効率の転写キットも販売されているので,あえてそのプロトコールを変更することはお勧めできないが,現状に満足できないことがあれば,皆さんも条件を検討してみてはどうだろうか.
連載を終えて
6回の連載を通して本シリーズでは,核酸のエタノール沈殿や電気泳動,そして転写など,核酸断片を扱う研究者にとってはすでにルーティンワークになっている手法についてその原理と手法を再考してみた.普段何気なく行っている操作でも,その理由を考えてみると意外に気付いていなかったこともあり,著者らも本シリーズを通して改めて研究の奥深さに触れることができた次第である.最近は装置や試薬キットなどが充実し,ルーティンに結果を出せる研究が増えてきたが,時には自分の行っている実験を振り返り,細かな点を気にしてみてはいかがだろうか.新たな発見にはそのような遠回りも必要かもしれない.
- ※この連載は実験医学 2008年8月号に掲載されたものです
Profile
- 劉 爽(Shuang Liu)
- 理化学研究所生命分子システム基盤研究領域
- 香川 亜子(Ako Kagawa)
- タグシクス・バイオ株式会社
- 木本 路子(Michiko Kimoto)
- 理化学研究所生命分子システム基盤研究領域
- 平尾 一郎(Ichiro Hirao)
- 理化学研究所生命分子システム基盤研究領域/タグシクス・バイオ株式会社